🚀 1.0.0 发布
visPedigree 是一款基于 R 语言开发的系谱分析与可视化工具,旨在解决动植物育种中复杂系谱结构的展示难题。
随着育种群体规模的扩大,传统工具在处理大规模系谱,特别是水产动物大家系系谱时,时常面临计算缓慢、可视化困难等问题。为此,visPedigree 1.0.1 进行了底层架构的全面重构。新版本引入 C++ (Rcpp) 对矩阵运算和近交系数计算等密集型任务进行底层加速,显著提升了计算效率;同时,利用图论算法 (Graph Theory) 优化了系谱整理逻辑,实现了世代自动推断与逻辑错误(如 Loop)的高效检测。
本文将介绍该版本的主要功能更新,包括焦点个体追踪、近交系数可视化及新增的矩阵分析工具。
✨ 主要功能更新
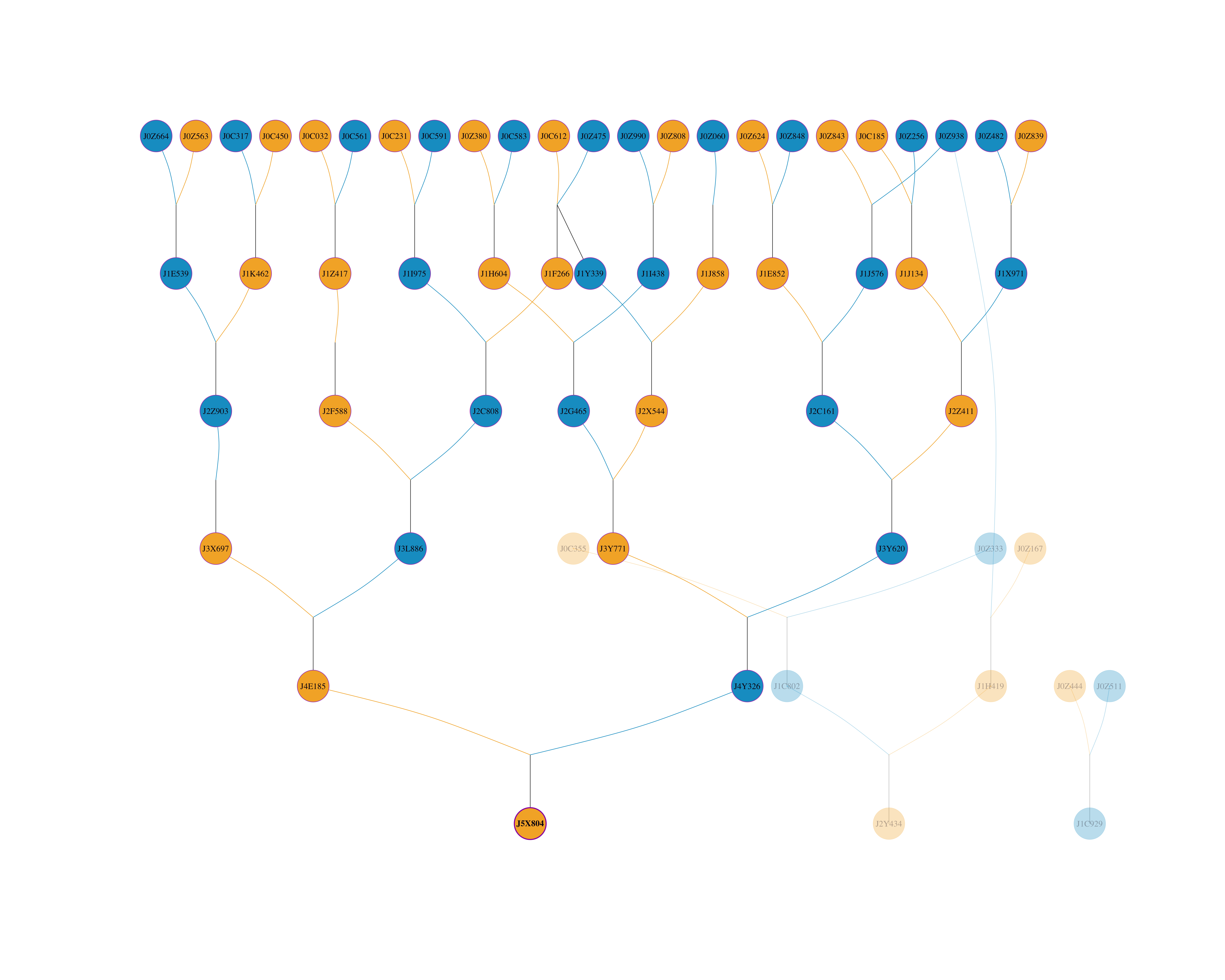
1. 动态焦点追踪 (Focus & Trace)
在大规模群体中,快速定位特定个体及其血缘脉络是系谱分析的常见需求。新版本引入了交互式的 highlight 和 trace 参数,支持对核心个体及其祖先或后代进行针对性展示。
highlighttrace
"up": 仅追踪并显示其祖先节点。"down": 仅追踪并显示其后代节点。"all": 同时追踪祖先与后代。
# 安装并加载 # devtools::install_github("luansheng/visPedigree") library (visPedigree)data (simple_ped)# 场景:高亮显示个体 "J5X804" 并追踪其所有祖先 <- tidyped (simple_ped, genmethod = "bottom" )visped (tidy_ped, highlight = "J5X804" , trace = "up" , cex = 0.5 , symbolsize = 10 )
2. 增强的数据预处理 (tidyped)
tidyped 函数不仅用于数据清洗,现在还集成了强大的诊断与统计功能:
逻辑错误诊断 : 利用图论算法自动检测系谱中的死循环 (Loops) 和重复条目。深度数据摘要 : 通过 summary() 方法,提供系谱深度、世代重叠度、每代近交水平等详细统计信息。系谱修剪 (prune) : 自适应保留有效核心群体。
# 检测系谱死循环 try (tidyped (loop_ped))
Error : Pedigree error! Pedigree loops detected:
M -> P -> R -> T -> V -> M
F -> E -> C -> A -> F
# 数据清洗与近交计算 <- tidyped (simple_ped, inbreed = TRUE )# 查看系谱统计摘要 summary (dt_ped)
Pedigree Summary
================
Total Individuals: 59
- Males: 29 (49.2%)
- Females: 30 (50.8%)
Pedigree Structure:
- Founders (no parents): 28
- Both parents known: 28
- Sire only known: 2
- Dam only known: 1
Generation:
- Maximum: 6
- Distribution:
Gen 1: 28 individuals
Gen 2: 16 individuals
Gen 3: 8 individuals
Gen 4: 4 individuals
Gen 5: 2 individuals
Gen 6: 1 individuals
Reproduction:
- Individuals with offspring: 56
- Sires: 28 (Mean=1.1, Max=2 offspring)
- Dams: 28 (Mean=1.0, Max=2 offspring)
Full-sibling Families:
- Number of families: 27
- Mean family size: 1.04
- Maximum family size: 2
- Top families by size:
J0Z475xJ0C612: 2
J0C317xJ0C450: 1
J0C561xJ0C032: 1
J0C583xJ0Z380: 1
J0C591xJ0C231: 1
Inbreeding Coefficients:
- All individuals:
Mean = 0.0001, Min = 0.0000, Max = 0.0039
Inbred (f > 0): 1 (1.7%)
================
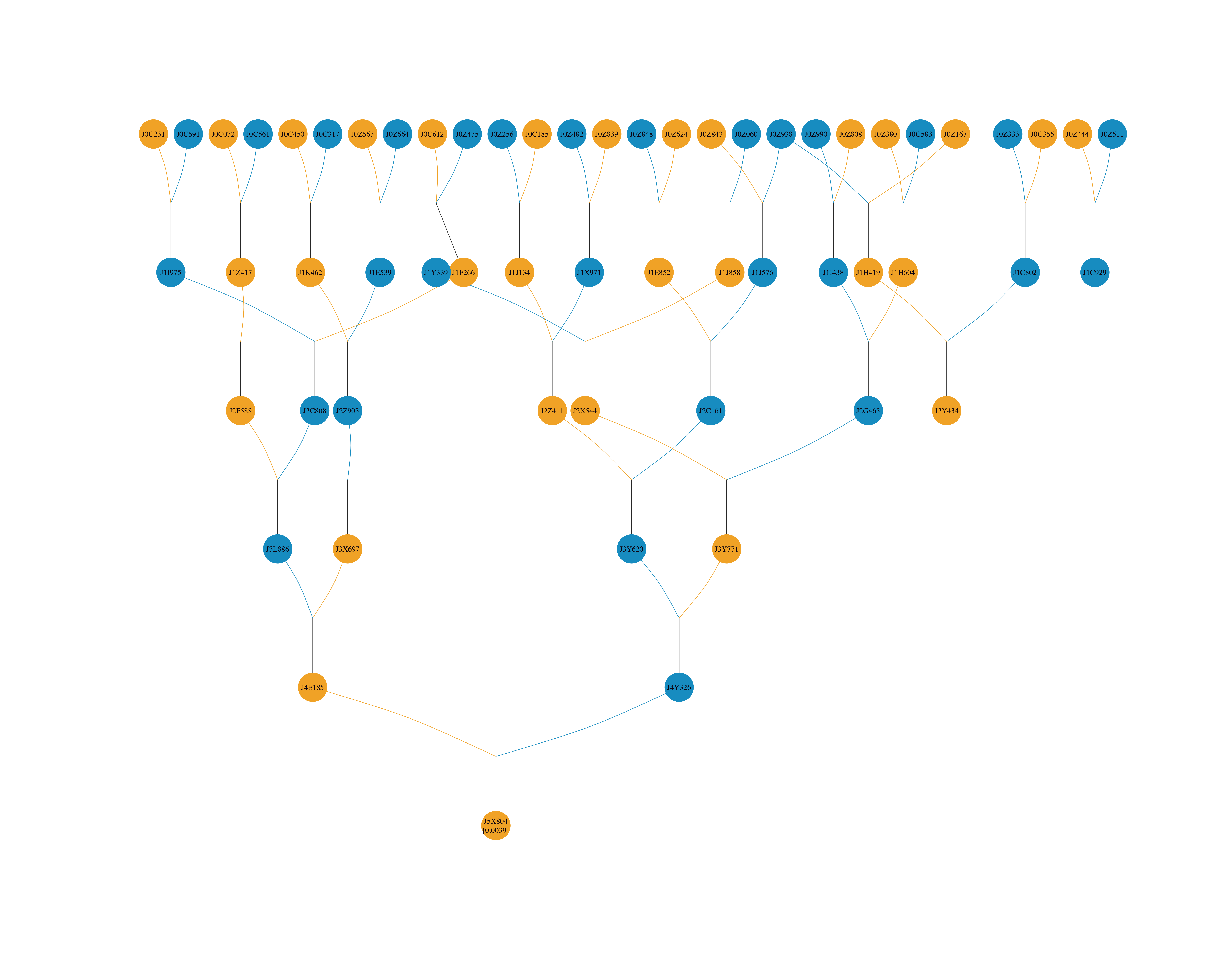
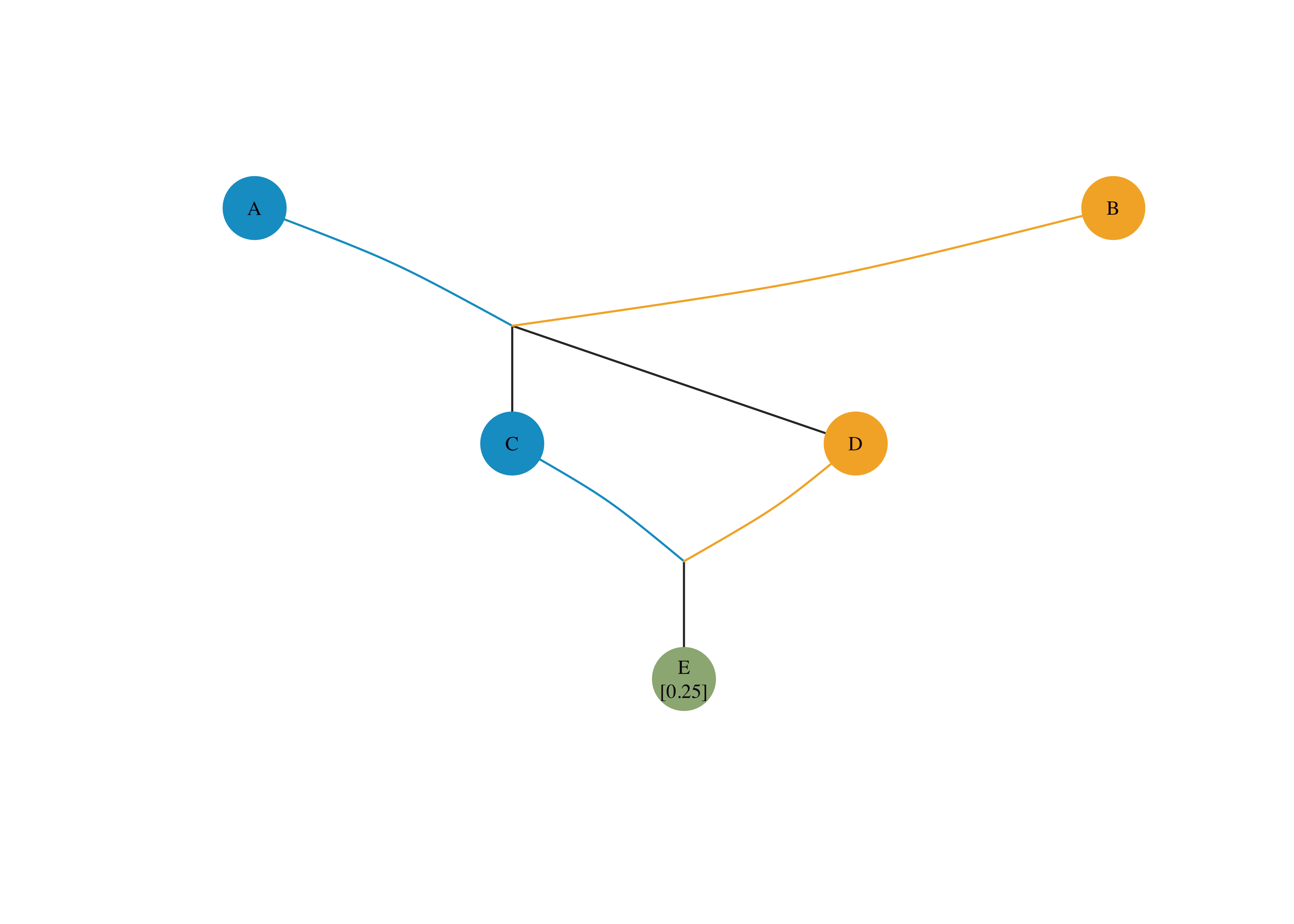
3. 近交系数可视化 (Inbreeding Visualization)
控制近交水平是制定育种方案的关键。visPedigree 1.0.0 将近交系数 (\(F\) ) 的计算与可视化进行了整合。用户可在数据整理阶段直接计算 \(F\) 值,并在绘图时将其直观标注在个体节点上。
tidyped(..., inbreed = TRUE)visped(..., showf = TRUE)\(F\) 值。
# 整理系谱并计算近交系数 <- tidyped (simple_ped, inbreed = TRUE )# 绘图时显示近交系数 visped (DT_ped, showf = TRUE , cex = 0.45 , symbolsize = 10 )
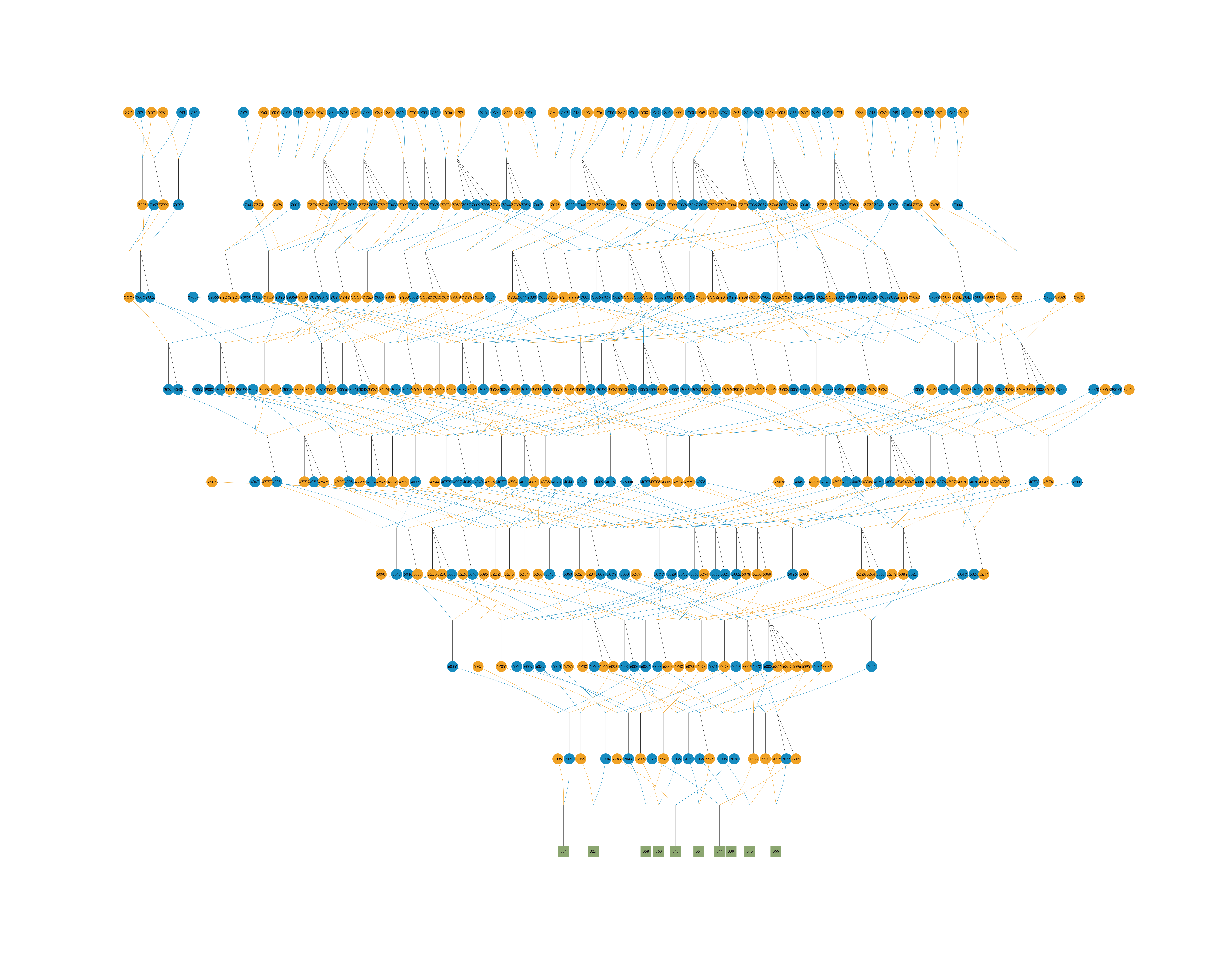
4. 系谱图压缩模式 (Compact Mode)
在水产育种等高繁殖力物种的场景中,全同胞家系(Full-sib family)往往包含大量个体。如果不加处理直接绘图,图像会横向无限延伸,导致关键结构难以辨识。
visPedigree 提供了 compact = TRUE 参数,专门针对全同胞家系进行了可视化优化。开启该模式后,同一全同胞家系的后代将被“折叠”展示,极大缩减了绘图宽度,使整体系谱结构更加紧凑、清晰。 visPedigree设计函数时,考虑了对管道符|>的支持,简化代码量,逻辑性更强。
# 1. 系谱清洗并自动分割独立群体(GP1 为最大的连通群体) <- big_family_size_ped |> tidyped () |> splitped ()<- ped_groups$ GP1# 2. 选取最后 10 个家系的个体作为目标,演示系谱修剪 (Pruning) # 使用 data.table 的语法确保高效提取 <- tail (unique (maxi_group$ Family), 10 )<- maxi_group[Family %in% last_10_fams, Ind]# 3. 提取目标个体的完整血缘脉络,并开启 Compact 模式展示 # Compact 模式会将全同胞家系“折叠”,极大提升了大规模家系的可视化清晰度 |> tidyped (cand = cands, genmethod= "bottom" ) |> visped (compact = TRUE , cex = 0.3 )
🛠️ 矩阵分析工具
除核心的可视化功能外,visPedigree 还提供了一系列辅助育种分析的工具函数,支持从系谱数据中提取关键遗传信息。
1. 亲缘关系矩阵计算 (pedmat)
pedmat() 函数利用 C++ 加速,可高效计算亲缘关系矩阵 (Numerator Relationship Matrix, A-Matrix) 或近交系数向量。
它同样支持 compact 参数。在水产育种等场景下,如果不需要针对每个个体计算矩阵,pedmat(..., compact=TRUE) 可以输出全同胞家系层面的亲缘关系矩阵,这将矩阵维度从个体级(数万行)降低到家系级(数百行),极大地节省了内存和后续遗传评估的计算时间。
# 计算个体级稀疏 A 矩阵 <- pedmat (simple_ped, method = "A" , sparse = TRUE )# 计算家系级压缩 A 矩阵 (Compact Mode) <- pedmat (simple_ped, method = "A" , compact = TRUE )
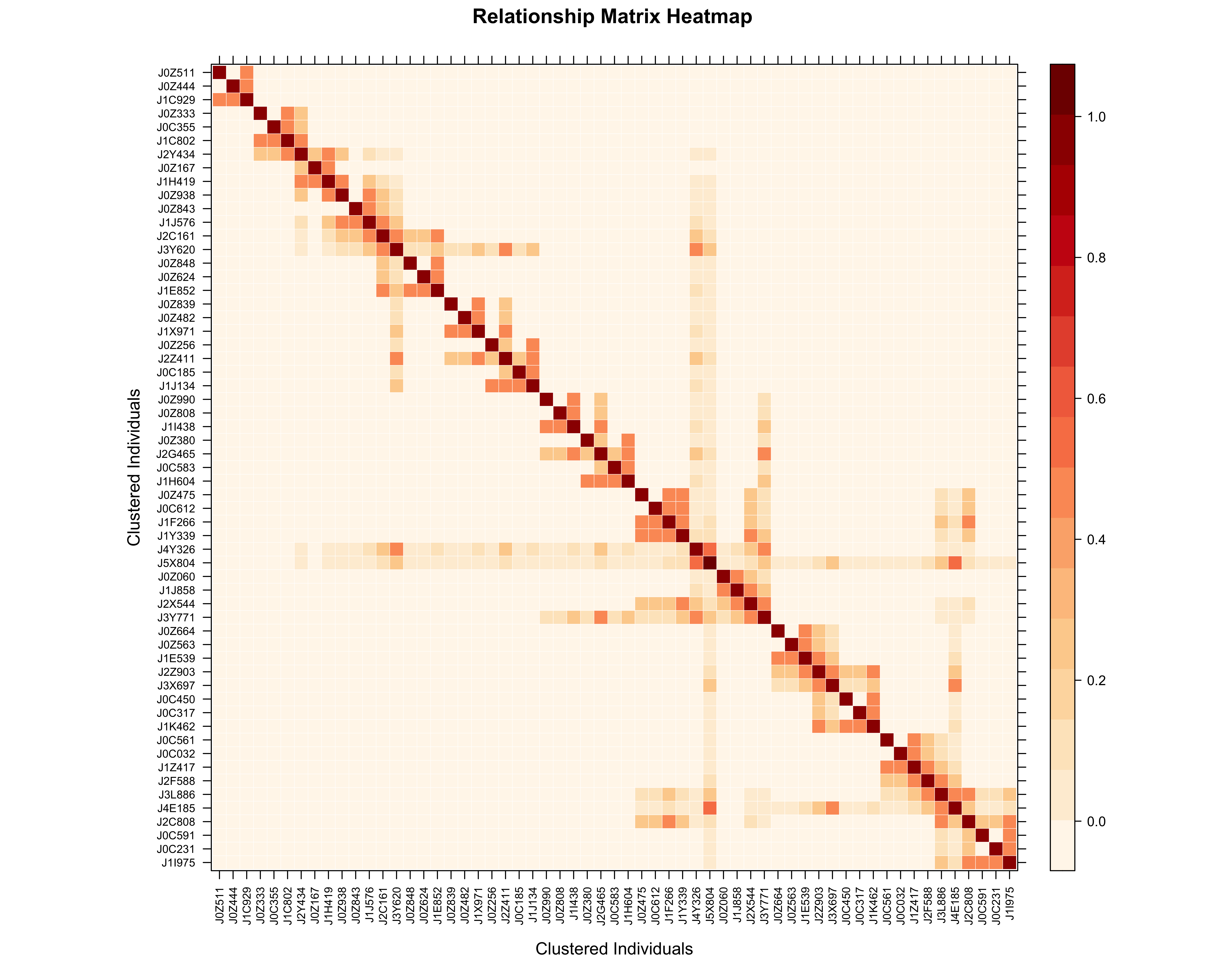
2. 矩阵可视化 (vismat)
vismat() 专门用于可视化亲缘关系矩阵。通过热图 (Heatmap) 的形式,直观展示群体内部的亲缘结构,有助于快速识别家系聚类和潜在的近交风险。
# 可视化 A 矩阵 vismat (A_ind, labelsize= 0.5 )
💡 快速上手 (Quick Start)
visPedigree 遵循 Tidy Data 原则。无论原始数据是否存在缺失或乱序,tidyped() 均可将其标准化为符合分析要求的格式。
library (visPedigree)library (data.table)# 1. 准备示例数据 <- data.table (ID = c ("A" , "B" , "C" , "D" , "E" ),Sire = c (NA , NA , "A" , "A" , "C" ),Dam = c (NA , NA , "B" , "B" , "D" )# 2. 数据清洗 (补全、排序、计算近交) <- tidyped (ped, inbreed = TRUE )# 3. 可视化展示 visped (tidy_ped, showf = TRUE )
快速入手的最便捷途径,是阅读viPedigree包的3个vignette,可以在该包pkgdowns 站点 的Articles中找到。
📥 获取与反馈
visPedigree 1.0.1 源代码及文档已托管至 GitHub。
visPedigree 1.0.1 已在 CRAN 上发布。
CRAN : install.packages("visPedigree")
欢迎使用者通过 GitHub Issue 反馈使用问题或提出功能建议。
Citation: Luan, S. (2026). visPedigree: Visualization and Analysis of Pedigrees. R package version 1.0.1. https://doi.org/10.32614/CRAN.package.visPedigree